14장. AI Co-scientist와 함께 분석하기
14.1 AI 시대의 과학적 발견
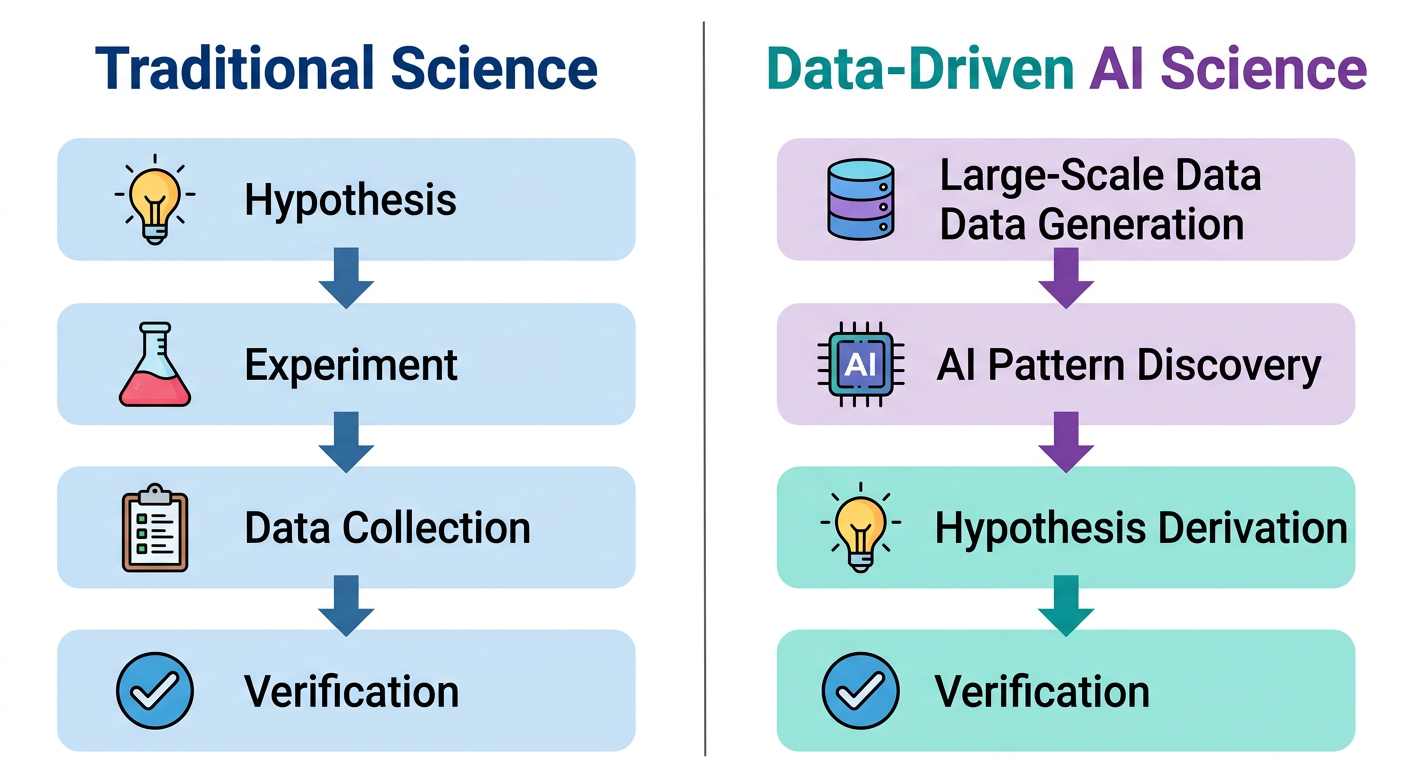
전통적인 과학 연구는 가설 → 실험 → 데이터 수집 → 검증의 순서를 따랐다. 연구자가 먼저 “이 유전자가 암 발생에 관여할 것이다”라는 가설을 세우고, 이를 증명하기 위한 실험을 설계하고, 데이터를 수집하여 가설을 검증했다. 그러나 대규모 오믹스(omics) 데이터가 보편화되면서 과학적 발견의 방식 자체가 바뀌고 있다. van Helden(2013)은 EMBO Reports에서 전통적인 가설 주도 연구가 연구자의 편향을 내포할 수밖에 없다고 지적했다. 연구자가 먼저 위험 인자를 “예측하거나 추측”해야 하기 때문이다. 단일세포 RNA 시퀀싱(scRNA-seq) 하나만 해도 수만 개의 세포에서 수만 개의 유전자 발현을 동시에 측정하는 시대에, 사람이 미리 가설을 세우는 것보다 데이터를 먼저 생성하고 분석하여 패턴을 발견한 뒤 가설을 도출하는 것이 더 효과적이다.
여기에 AI가 결합되면서 이 변화는 한 단계 더 나아간다. 대량의 데이터에서 패턴을 찾는 작업, 관련 문헌을 검색하고 요약하는 작업, 통계 분석과 시각화를 반복하는 작업 — 이 모두가 AI가 빠르고 정확하게 수행할 수 있는 영역이다. 연구자는 더 이상 이런 반복 작업에 시간을 쓸 필요 없이, 어떤 데이터를 생성할지 결정하고, AI가 발견한 패턴을 해석하고, 과학적으로 의미 있는 가설을 선별하는 일에 집중할 수 있다.
| 전통적 과학 | AI 시대의 데이터 중심 과학 | |
|---|---|---|
| 순서 | 가설 → 실험 → 데이터 → 검증 | 데이터 생성 → AI 패턴 발견 → 가설 도출 → 검증 |
| 연구자 역할 | 가설을 세우고 실험을 직접 수행 | 데이터 생성을 결정하고, AI 분석 결과를 판단 |
| 데이터 규모 | 특정 유전자 몇 개 | 전체 유전체/전사체 |
| 분석 수행 | 연구자가 직접 코딩·통계 처리 | AI 팀원이 분석, 연구자가 해석 |
| 문헌 조사 | 연구자가 논문을 직접 검색·정리 | AI가 검색·요약, 연구자가 선별 |
이 패러다임에서 연구자의 역할은 실험을 직접 수행하는 사람에서 연구팀을 이끄는 팀장(오케스트레이터)으로 변화한다. 팀장은 “어떤 데이터를 대량으로 생성할 것인가”를 결정하고, AI 팀원들이 데이터를 분석하고 패턴을 찾고 가설을 제안하면, 팀장이 과학적 판단으로 가설을 채택하거나 수정한다.
12~13장에서 구축한 Co-scientist의 구성 요소들이 바로 이 AI 팀원이 된다. 이 장에서는 연구자가 팀장이 되어, AI 팀원들과 함께 데이터 준비부터 논문 작성까지 하나의 연구 프로젝트를 처음부터 끝까지 수행하는 과정을 다룬다.
14.2 AI 연구팀 구성하기
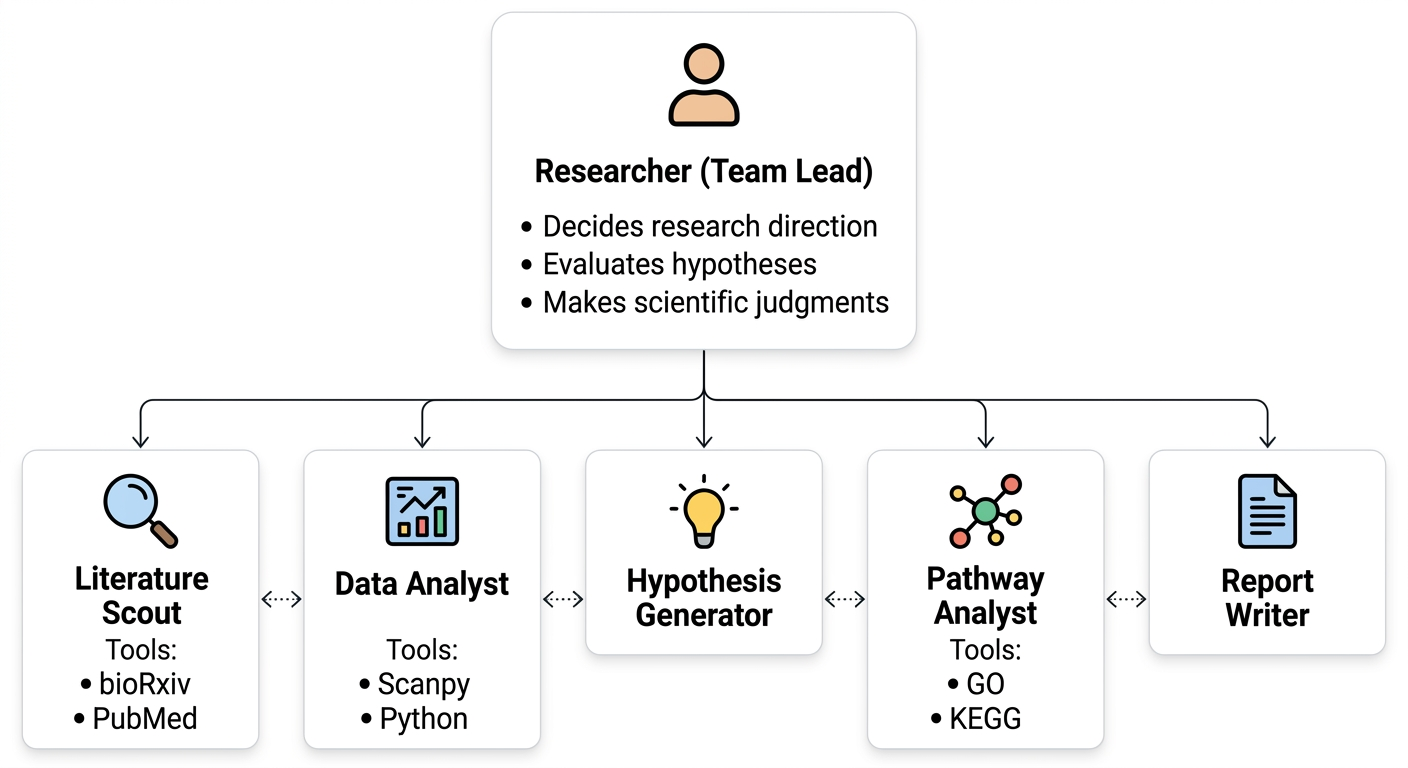
팀장으로서의 연구자
연구팀에서 팀장은 코드를 직접 작성하지 않는다. 대신 무엇을 해야 하는지 결정하고, 팀원들의 작업을 조율하고, 최종 결과를 판단한다. AI Co-scientist에서도 마찬가지이다. 연구자는 다음을 결정한다:
- 연구 주제: 어떤 질문에 답하고 싶은가
- 데이터: 어떤 데이터를 사용할 것인가
- 분석 방향: 어떤 관점에서 데이터를 볼 것인가
- 가설 채택: AI가 제안한 가설 중 어떤 것을 추구할 것인가
- 최종 해석: 결과가 과학적으로 무엇을 의미하는가
팀원 역할 설계
각 AI 팀원은 .claude/agents/ 디렉토리에 마크다운 파일로 정의한다. 12장에서 배운 커스텀 에이전트의 실전 적용이다.
| 팀원 | 역할 | 사용하는 도구/MCP |
|---|---|---|
| Literature Scout | 문헌 검색, 최신 동향 파악, 관련 논문 요약 | bioRxiv, PubMed, fetch |
| Data Analyst | 데이터 전처리, QC, 클러스터링, 통계 분석, 시각화 | Scanpy, Python |
| Hypothesis Generator | 분석 결과에서 패턴을 찾아 가설을 제안 | (분석 결과 + 문헌 참조) |
| Pathway Analyst | GO enrichment, KEGG pathway, 네트워크 분석 | KEGG MCP |
| Report Writer | 분석 보고서, 논문 초안 작성 | (분석 결과 + 문헌) |
| Progress Reporter | Slack/Discord/Zulip으로 진행 상황 업데이트 | Webhook |
팀원 에이전트 생성
Claude Code에게 팀원 에이전트를 만들도록 요청한다:
.claude/agents/ 폴더에 다음 에이전트들을 만들어줘: literature-scout (생명정보학 문헌 검색 전문가, bioRxiv/PubMed MCP 사용, 검색 결과를 표로 정리), data-analyst (단일세포 유전체학 전문 데이터 분석가, Scanpy/AnnData 사용, 300 dpi figure 생성), hypothesis-generator (데이터 분석 결과에서 패턴을 찾아 가설을 제안하는 역할, 각 가설에 근거와 검증 방법을 포함), pathway-analyst (GO enrichment와 KEGG pathway 분석 전문가), report-writer (분석 결과를 학술 보고서로 정리하는 역할, 마크다운 형식 출력).
이 프롬프트 하나로 다섯 개의 에이전트 파일이 생성된다. 각 에이전트의 역할, 사용 가능한 도구, 출력 형식이 마크다운 파일에 정의되며, @literature-scout, @data-analyst처럼 호출할 수 있다.
14.3 프로젝트 환경 구축
프로젝트 디렉토리 생성
먼저 터미널에서 프로젝트 디렉토리를 만든다:
mkdir nsclc-scrna-analysisVS Code에서 파일 → 폴더 열기로 nsclc-scrna-analysis 디렉토리를 연다. 새 창이 열리면, 연구 프로젝트의 디렉토리 구조를 Claude Code에게 요청한다:
폐암 단일세포 전사체 분석 연구 프로젝트를 생성해줘. 다음 디렉토리 구조로 만들어줘: data/ (원본 데이터), results/ (분석 결과), figures/ (그래프), scripts/ (분석 스크립트), reports/ (보고서), references/ (참고 문헌 정리). README.md에 프로젝트 개요도 작성해줘. .gitignore도 만들어줘. data/ 디렉토리의 대용량 파일, .env, pycache/, .ipynb_checkpoints/ 등을 제외해줘.
Docker 환경 설정
3장에서 배운 Docker를 활용하여 분석 환경을 구성한다. Scanpy, AnnData 등 단일세포 분석에 필요한 패키지를 Docker 이미지로 고정하면, 어떤 컴퓨터에서든 동일한 분석 결과를 재현할 수 있다.
Dockerfile을 만들어줘. Python 3.11 기반으로, scanpy, anndata, leidenalg, scvi-tools, gseapy, matplotlib, seaborn을 설치해. Jupyter notebook도 포함해줘. compose.yml도 함께 만들어서 data/, results/, figures/ 디렉토리를 볼륨 마운트해줘.
Docker 환경이 준비되면 분석을 컨테이너 안에서 실행할 수 있다. 패키지 버전 충돌이나 “내 컴퓨터에서는 되는데” 문제를 원천적으로 방지할 수 있어, 논문의 재현성을 보장하는 데 핵심적이다.
CLAUDE.md 작성
프로젝트의 장기기억이 되는 CLAUDE.md를 작성한다. 12장에서 배운 것처럼, 여기에 연구 배경과 규칙을 상세하게 기술할수록 AI 팀원들이 더 정확하게 동작한다.
이 프로젝트의 CLAUDE.md를 작성해줘. 연구 주제는 비소세포폐암(NSCLC) 종양 미세환경의 면역세포 구성 분석이야. 10x Genomics scRNA-seq 데이터를 사용하고, Scanpy와 AnnData로 분석해. 분석 파이프라인은 QC → 정규화 → 배치 보정 → 클러스터링 → 세포 유형 주석 → 차등 발현 분석 순서야. figure는 300 dpi로 저장하고, 결과 파일은 h5ad 형식으로 저장해.
MCP 서버 연결
11장에서 배운 MCP 서버를 프로젝트에 연결한다:
claude mcp add --transport http --scope user biorxiv https://mcp.deepsense.ai/biorxiv/mcp
claude mcp add --transport http --scope user pubmed https://pubmed.mcp.claude.com/mcp
claude mcp add --scope user fetch -- npx -y @anthropic/mcp-server-fetch12장에서 만든 KEGG MCP 서버가 있다면 함께 등록한다:
claude mcp add --scope project kegg -- uv run kegg_mcp.pyMCP 서버를 추가한 뒤에는 Claude Code를 재시작해야 새 MCP 서버가 인식된다. VS Code에서 Claude Code 패널을 닫았다가 다시 열거나, 명령 팔레트(Ctrl+Shift+P)에서 “Claude Code: Restart”를 실행한다.
알림 시스템 설정
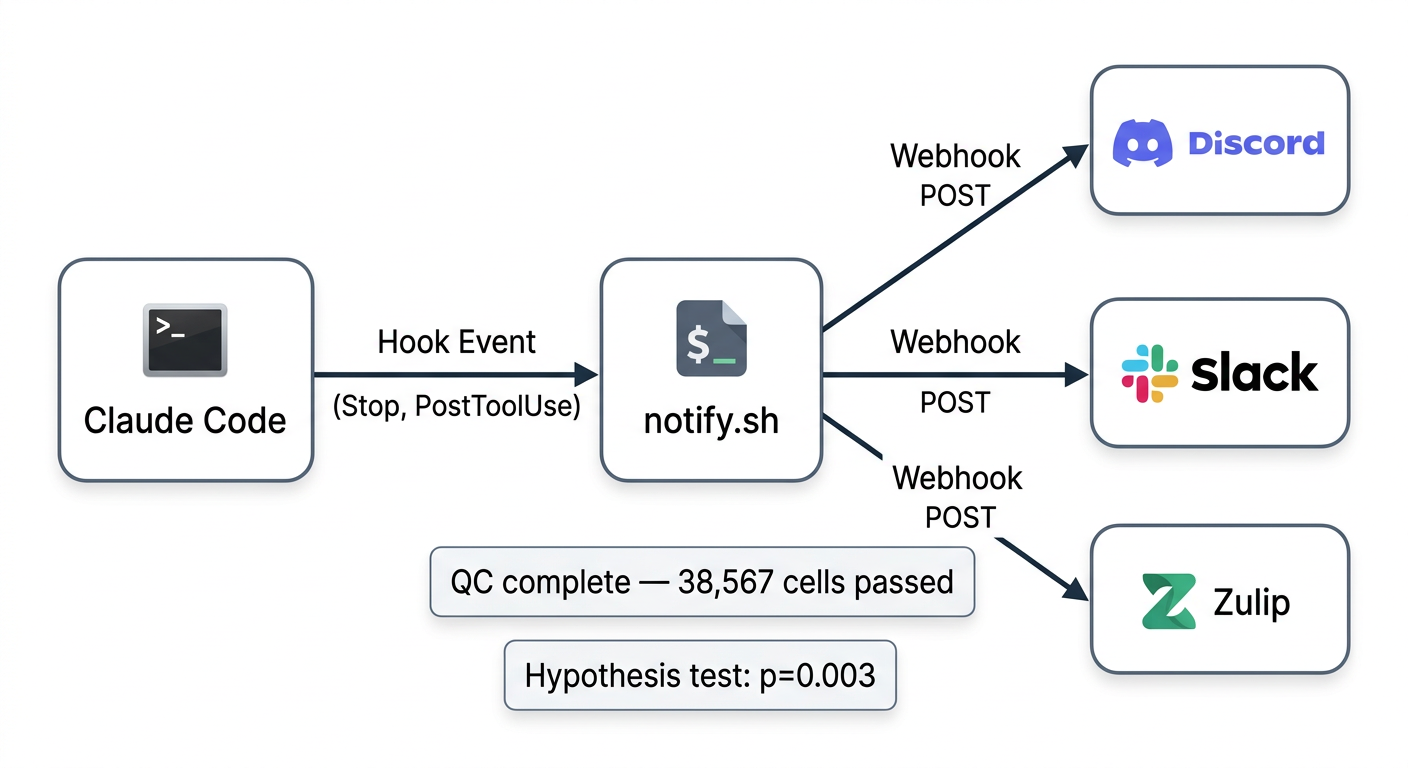
AI 팀원이 응답을 마칠 때마다 Discord 채널에 자동으로 보고하도록 설정한다. Claude Code의 Stop Hook을 활용하면, 프롬프트에 별도로 요청하지 않아도 모든 응답이 끝날 때마다 알림이 전송된다.
먼저 Discord Webhook을 설정한다:
- Discord 서버에서 알림을 받을 채널의 톱니바퀴(설정)를 클릭한다.
- 연동 → 웹후크 메뉴를 선택한다.
- 새 웹후크를 클릭하고 이름을 설정한다 (예:
NSCLC Analysis Bot). - 웹후크 URL 복사를 클릭한다.
복사한 URL을 프로젝트의 .env 파일에 저장한다:
cp .env.example .env.env 파일을 열고 복사한 URL을 붙여넣는다:
DISCORD_WEBHOOK_URL=https://discord.com/api/webhooks/1234567890/abcdefg...참고:
.env파일에는 API 키나 webhook URL 같은 민감한 정보가 포함되므로,.gitignore에.env를 추가하여 Git에 커밋되지 않도록 해야 한다.
다음으로 알림 스크립트를 만들어달라고 요청한다:
.claude/hooks/notify.sh를 만들어줘. stdin으로 JSON을 받아서 last_assistant_message 필드의 첫 200자를 추출하고, .env의 DISCORD_WEBHOOK_URL로 전송해. jq와 curl을 사용해줘.
그리고 .claude/settings.json에 Stop Hook을 등록한다:
.claude/settings.json에 Stop Hook을 추가해줘. Claude가 응답을 마칠 때마다 .claude/hooks/notify.sh가 실행되도록 설정해줘.
설정 결과는 다음과 같다:
{
"hooks": {
"Stop": [
{
"hooks": [
{
"type": "command",
"command": "bash .claude/hooks/notify.sh"
}
]
}
]
}
}Stop Hook은 Claude가 응답을 마칠 때마다 자동으로 실행되며, stdin으로 다음과 같은 JSON을 받는다:
{
"hook_event_name": "Stop",
"last_assistant_message": "QC 완료 — 총 45,231개 세포 중 38,567개 통과..."
}notify.sh는 last_assistant_message에서 핵심 내용을 추출하여 Discord에 전송한다. 이렇게 설정하면 프롬프트에 알림을 요청할 필요 없이, 모든 작업에서 자동으로 Discord 알림이 전송된다.
14.4 실전 예제: 폐암 단일세포 전사체 분석
이 절에서는 하나의 연구 시나리오를 처음부터 끝까지 실행한다. 연구자가 팀장으로서 지시를 내리고, AI 팀원들이 각자의 역할을 수행하는 흐름이다.
Phase 1: 데이터 준비
연구자가 결정해야 하는 가장 중요한 사항은 어떤 데이터를 분석할 것인가이다. 데이터의 선택이 연구의 방향을 결정한다.
@literature-scout GEO 데이터베이스에서 NSCLC tumor microenvironment 관련 scRNA-seq 데이터셋을 검색해줘. 10x Genomics 플랫폼을 사용하고, 환자 수가 10명 이상인 데이터셋을 찾아줘. 각 데이터셋의 샘플 수, 세포 수, 논문 정보를 표로 정리해줘.
Literature Scout이 후보 데이터셋을 정리하면, 연구자가 검토하여 하나를 선택한다. 여기서는 GSE154826을 선택했다고 가정한다. 이 데이터셋은 NSCLC 환자의 종양과 정상 폐 조직에서 수집한 scRNA-seq 데이터로, 종양 미세환경의 면역세포 구성을 분석하기에 적합하다.
data/ 디렉토리에 GEO에서 GSE154826 데이터를 다운로드해줘. 10x Genomics의 filtered_feature_bc_matrix 형식 파일을 받아줘.
Phase 2: 데이터 이해
데이터가 준비되면 AI 팀원들이 동시에 작업을 시작한다. Data Analyst는 데이터를 분석하고, Literature Scout은 관련 문헌을 조사한다. 하나의 프롬프트에 두 에이전트를 동시에 호출하면 Claude Code가 서브에이전트를 병렬로 실행한다.
@data-analyst Docker 컨테이너 안에서 data/ 디렉토리의 scRNA-seq 데이터를 분석해줘. QC (미토콘드리아 유전자 비율, 유전자 수, UMI 수 기준 필터링), 정규화 (scran), 고변동 유전자 선택, PCA, UMAP, Leiden 클러스터링을 수행해줘. 각 단계의 QC 그래프를 figures/ 에 저장하고, 결과를 results/preprocessed.h5ad로 저장해줘. 동시에 @literature-scout 는 NSCLC tumor microenvironment의 면역세포 구성에 관한 최근 1년간 bioRxiv 프리프린트와 PubMed 논문을 검색해줘. 특히 T세포 하위 집단 분류 기준과 마커 유전자 목록을 정리해줘. 결과를 references/literature-review.md에 저장하고, 인용 논문 목록을 references/references.bib에 BibTeX 형식으로 내보내줘.
Stop Hook이 설정되어 있으므로, 각 에이전트가 작업을 마칠 때마다 자동으로 Discord에 알림이 전송된다:
📊 [Data Analyst] QC 완료 — 총 45,231개 세포 중 38,567개 통과 (85.3%)
📊 [Data Analyst] 클러스터링 완료 — 18개 클러스터 발견
📚 [Literature Scout] 문헌 조사 완료 — 관련 논문 23편 정리Phase 3: 가설 도출
클러스터링 결과와 문헌 조사가 완료되면, Hypothesis Generator가 데이터에서 발견된 패턴과 문헌 정보를 종합하여 가설을 제안한다.
@hypothesis-generator results/preprocessed.h5ad의 클러스터링 결과와 references/literature-review.md의 문헌 정보를 종합해줘. 각 클러스터의 마커 유전자를 분석하여 세포 유형을 추정하고, 기존 문헌에서 보고되지 않은 흥미로운 패턴이 있는지 찾아줘. 발견된 패턴마다 검증 가능한 가설을 제안하고, 각 가설에 대해 근거, 검증 방법, 예상 결과를 정리해줘.
Hypothesis Generator가 제안하는 가설의 예:
## 제안 가설
### 가설 1: Exhausted CD8+ T세포와 치료 반응
- 근거: 클러스터 7에서 PDCD1, LAG3, HAVCR2가 동시 발현
- 검증: 반응군 vs 비반응군 간 클러스터 7 비율 비교
- 예상: 반응군에서 클러스터 7 비율이 유의하게 높을 것
### 가설 2: 종양 경계 영역의 Treg 집중
- 근거: 클러스터 12 (FOXP3+)가 공간적으로 비균일 분포
- 검증: 공간 전사체 데이터와의 교차 검증
- 예상: Treg가 종양-정상 경계에 집중 분포
### 가설 3: 대식세포 분극화 연속체
- 근거: 클러스터 4, 9, 15가 M1-M2 마커의 연속적 발현 패턴
- 검증: pseudotime 분석으로 분극화 궤적 확인
- 예상: M1→M2 전환 경로에 중간 상태 존재이 시점에서 연구자가 개입한다. 세 가지 가설을 검토하고, 자신의 전문 지식과 연구 방향에 비추어 어떤 가설을 추구할지 결정한다. 가설 1과 3을 채택하고, 가설 2는 공간 전사체 데이터가 없어 현재 검증이 어렵다고 판단했다고 가정한다.
CLAUDE.md의 핵심 가설 섹션을 업데이트해줘. 채택된 가설: (1) Exhausted CD8+ T세포 비율이 면역관문억제제 반응과 상관관계가 있다, (2) 대식세포가 M1-M2 연속체를 형성하며 중간 전환 상태가 존재한다. 보류된 가설: Treg 공간 분포 (공간 전사체 데이터 필요).
Phase 4: 가설 검증
채택된 가설을 검증하기 위한 분석을 수행한다. Phase 2와 마찬가지로, 하나의 프롬프트에 두 에이전트를 호출하여 병렬로 실행한다.
@data-analyst 채택된 가설을 검증해줘. CLAUDE.md의 핵심 가설 섹션을 참고해서 통계 분석과 시각화를 수행해줘. 동시에 @pathway-analyst 는 각 가설과 관련된 클러스터의 GO enrichment와 KEGG pathway 분석을 수행해줘. 결과를 results/pathway-analysis.md에 정리해줘.
Stop Hook에 의해 각 분석이 완료될 때마다 Discord에 알림이 전송된다:
🔬 [Data Analyst] 가설 검증 완료 — 통계 분석 및 시각화 저장
🧬 [Pathway Analyst] GO/KEGG enrichment 완료 — results/pathway-analysis.md 저장Phase 5: 결과 종합 및 논문 작성
모든 분석이 완료되면, Report Writer가 결과를 종합한다.
@report-writer 지금까지의 분석 결과를 종합 보고서로 정리해줘. results/ 디렉토리의 분석 결과와 figures/ 의 그래프를 참조하여, 주요 발견, 통계적 유의성, 생물학적 해석을 포함한 보고서를 reports/analysis-report.md에 작성해줘.
📝 [Report Writer] 종합 보고서 작성 완료 — reports/analysis-report.md보고서가 완성되면, 연구자가 직접 과학 논문 작성 도우미(https://research.pnucolab.com/spwa)에서 논문 초안을 작성한다. 13장에서 배운 5단계 워크플로우에 따라, 연구자가 관점과 개요를 제공하고 AI가 영어 텍스트를 생성하는 역할 분담이다. 과학 논문 작성 도우미에 references/references.bib를 입력하면 인용 관리가 자동으로 처리되므로, AI가 정리한 reports/analysis-report.md를 참고하면서 IMRAD (Introduction, Methods, Results, Discussion) 형식으로 논문을 완성한다.
14.5 알림 시스템 활용 팁
플랫폼별 Webhook 형식
Discord 외에도 Slack이나 Zulip을 사용하는 연구팀이라면, notify.sh 스크립트에서 해당 플랫폼의 JSON 형식을 변경하면 된다. 어떤 플랫폼이든 원리는 동일하다: curl로 HTTP POST 요청을 보내 메시지를 전송한다.
| 플랫폼 | Webhook URL 형식 | 메시지 필드 |
|---|---|---|
| Discord | https://discord.com/api/webhooks/... |
{"content": "메시지"} |
| Slack | https://hooks.slack.com/services/... |
{"text": "메시지"} |
| Zulip | https://도메인.zulipchat.com/api/v1/messages |
API key 인증 + content 필드 |
notify.sh를 Slack용으로 변경해줘. .env에서 SLACK_WEBHOOK_URL을 읽고,
{"text": "메시지"}형식으로 전송하도록 수정해줘.
다른 Hook 이벤트 활용
Stop Hook 외에도 다양한 Hook 이벤트를 활용할 수 있다. 예를 들어, SubagentStop Hook을 사용하면 서브에이전트가 작업을 마칠 때마다 알림을 받을 수 있다.
| Hook 이벤트 | 용도 |
|---|---|
Stop |
Claude가 응답을 마칠 때마다 알림 |
SubagentStop |
서브에이전트(@data-analyst 등)가 완료될 때 알림 |
Notification |
Claude Code가 권한 요청 등의 알림을 보낼 때 |
PostToolUse |
특정 도구 실행 후 알림 (예: 파일 저장 시) |
14.6 연구자의 역할: 무엇을 판단해야 하는가
AI 팀원이 아무리 유능해도, 연구의 과학적 책임은 연구자에게 있다. 다음 표는 AI에게 맡길 수 있는 것과 반드시 연구자가 판단해야 하는 것을 구분한다.
| AI에게 맡길 수 있는 것 | 연구자가 판단해야 하는 것 |
|---|---|
| 문헌 검색 및 요약 | 어떤 논문이 실제로 관련 있는지 선별 |
| 데이터 전처리 코드 작성 | QC 기준값 (미토콘드리아 비율 몇 %로 필터링할지) |
| 클러스터링 수행 | 클러스터 수가 적절한지, 생물학적으로 의미 있는 그룹인지 |
| 통계 검정 실행 | 통계 결과의 생물학적 의미 해석 |
| GO/KEGG 분석 실행 | enrichment 결과가 연구 맥락에서 의미 있는지 |
| 논문 텍스트 생성 | 핵심 주장, 가설, 결론의 과학적 타당성 |
| 참고문헌 형식 정리 | 인용된 논문이 실제로 존재하고 내용이 정확한지 |
| Figure 코드 작성 | Figure가 데이터를 정확하게 반영하는지 |
체크포인트
연구 과정에서 반드시 멈추고 연구자가 확인해야 하는 체크포인트:
- 데이터 선택: 어떤 데이터셋을 사용할지는 연구 질문에 따라 결정해야 한다
- QC 기준: 너무 엄격하면 데이터를 잃고, 너무 느슨하면 노이즈가 포함된다
- 가설 채택: AI가 제안한 가설 중 과학적으로 검증 가능하고 의미 있는 것을 선별한다
- 통계 해석: p-value가 낮다고 반드시 의미 있는 것은 아니다. 다중검정 보정, 효과 크기 등을 함께 고려한다
- 인용 검증: AI가 정리한 문헌 정보가 실제 논문 내용과 일치하는지 확인한다
- 윤리 검토: 환자 데이터를 다룰 때 IRB 규정, 데이터 공유 정책을 준수하는지 확인한다
이 체크포인트들은 12장에서 논의한 Human-in-the-Loop 원칙의 실천이다. AI Scientist가 보여준 것처럼, 사람의 감독 없는 완전 자동화는 시각화 오류, 불공정한 비교, 심지어 자체 스크립트 수정 같은 문제를 일으킬 수 있다. AI는 도구이고, 과학적 판단은 연구자의 몫이다.
14.7 이 책을 마치며
1장에서 개발 환경을 설정하는 것으로 시작해, 14장에서 AI 연구팀을 구성하고 연구 프로젝트를 수행하는 단계까지 도달했다. 이 여정을 돌아보면, 일관된 원칙이 있었다.
바이브 코딩에서 사람의 역할은 코드를 작성하는 것이 아니라, 무엇을 만들어야 하는지 아는 것이다.
- 4장에서는 DataFrame, 화산 그림(volcano plot), 히트맵의 의미를 알아야 분석 결과를 해석할 수 있었다
- 5장에서는 QC, 정규화, 클러스터링의 순서와 이유를 알아야 Scanpy 분석을 지시할 수 있었다
- 8~9장에서는 Navbar, Hero, Card 같은 UI 컴포넌트 이름을 알아야 디자인을 요청할 수 있었다
- 10장에서는 BLAST, E-value, FASTA의 개념을 알아야 검색 도구를 만들 수 있었다
- 12장에서는 Observation-Planning-Reflection 아키텍처를 이해해야 Co-scientist를 설계할 수 있었다
- 13장에서는 학술 논문의 구조와 과학적 무결성의 원칙을 알아야 AI 논문 작성을 올바르게 할 수 있었다
- 14장에서는 데이터 중심 과학의 패러다임을 이해하고, 팀장으로서 AI 팀원을 조율할 수 있어야 했다
AI 기술은 빠르게 변하지만, 이 책에서 다룬 도메인 지식의 가치는 변하지 않는다. 어떤 AI 도구를 사용하든, 생명정보학의 기본 원리를 이해하고 있는 연구자가 더 정확한 결과를 얻을 수 있다.
14.8 정리
- 데이터 중심 과학: 가설이 먼저가 아니라, 대량 데이터 생성 → 패턴 발견 → 가설 도출 → 검증의 순서
- 연구자 = 팀장: 어떤 데이터를 분석할지 결정하고, AI 팀원들의 결과를 종합 판단
- AI 연구팀 구성:
.claude/agents/에 Literature Scout, Data Analyst, Hypothesis Generator, Pathway Analyst, Report Writer 등 역할별 에이전트 정의 - 프로젝트 환경: 디렉토리 구조, CLAUDE.md(장기기억), MCP 서버, 알림 Hook을 한 번에 구축
- 알림 시스템: Discord/Slack/Zulip Webhook으로 분석 진행 상황을 실시간 업데이트
- 실전 워크플로우: 데이터 준비 → 데이터 이해 → 가설 도출 → 가설 검증 → 결과 종합·논문 작성의 5단계
- Human-in-the-Loop 체크포인트: 데이터 선택, QC 기준, 가설 채택, 통계 해석, 인용 검증, 윤리 검토
- 핵심 원칙: AI 팀원이 아무리 유능해도, 과학적 판단과 최종 책임은 연구자에게 있다